| 前边两章讲完了RNAseq的一些概述,这一章节和下一章节讲解下ATACseq概述。 |
ATACseq概述
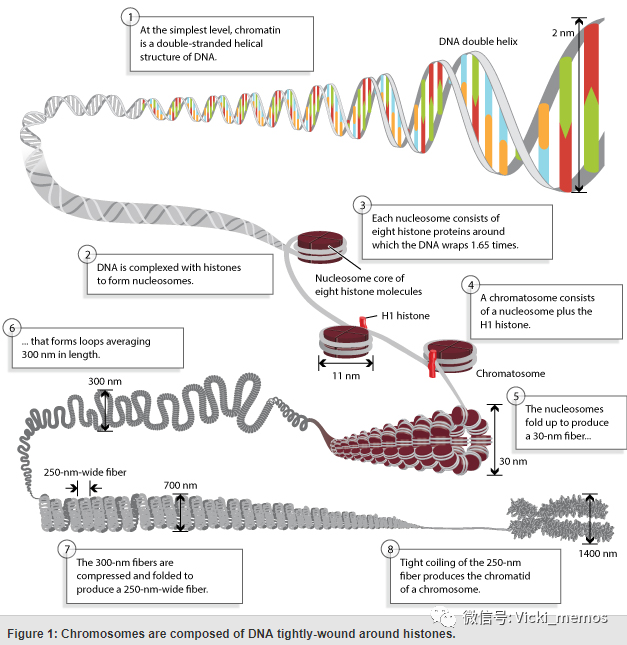
上图详细的展示了DNA(染色质)是如何从全长2 meter的长度折叠成纳米级至微米级的长度(染色体)。
How is DNA packaged?②
这样的结构特点:
折叠后的染色体可以更好的位于大小仅为1-20微米(低等植物细胞细胞核约1-4微米,高等植物细胞细胞核约5-20微米,高等动物细胞细胞核约5-20微米)的细胞核内。
如此长的染色质的折叠并不是仅仅靠本身就能完成的,还需要依赖几种不同组蛋白的协助形成串珠状(nucleosome),然后在H1组蛋白的协助下进一步折叠,2nm(碱基对)->11nm(nucleosome)->30nm(fiber)->300nm(U loops)->700nm+250nmwide(chromosome)。这就相当于你把织毛衣的毛线通过不同的缠绕方式缠绕成可以更好的放置的毛线球一样。
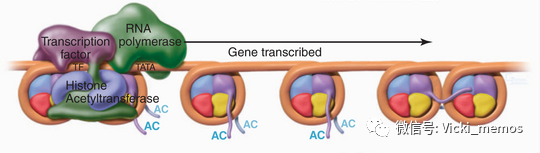
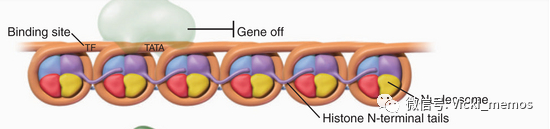
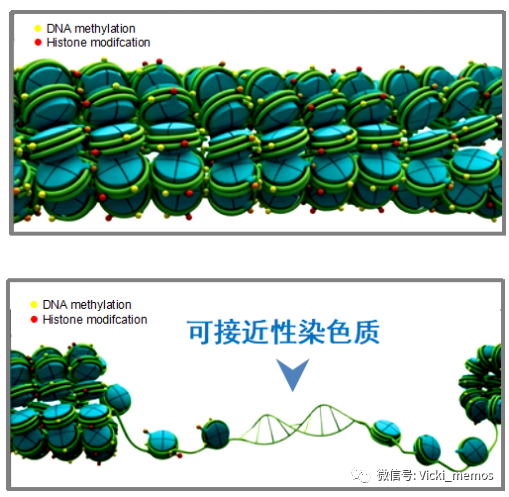
紧密缠绕的染色体状态的DNA(heterochromatin)是无法正常执行生命所需的转录翻译等活动的,是细胞中期的正常状态。但是在细胞分化,分裂等一些特定时期,需要执行特定转录翻译活动的时候,某些特定区域的紧致缠绕的DNA会解开这种折叠状态,允许某些调控元件(转录因子或者其他调控元件)结合到特定的区域,开始执行转录翻译活动,就像是你要打毛衣,需要解开缠绕的毛线球一样,如上图所示。
ATACseq测序
ATACseq应用
Reference:
① Annunziato, A. (2008) DNA Packaging: Nucleosomes and Chromatin. Nature Education 1(1):26.
https://www.nature.com/scitable/topicpage/dna-packaging-nucleosomes-and-chromatin-310/
②Cold Spring Harbor Laboratory-DNA LEARNING CENTER -Biology & 3D Anmation Library
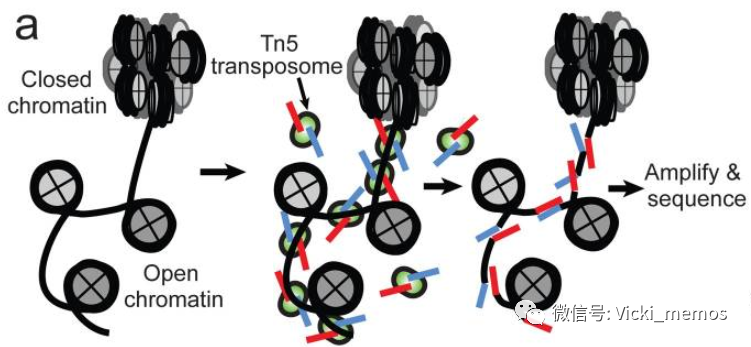
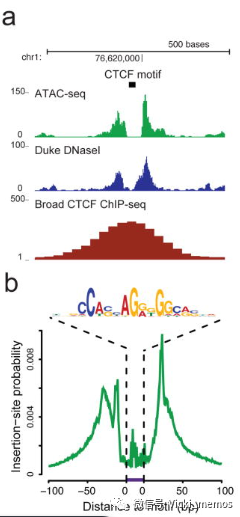
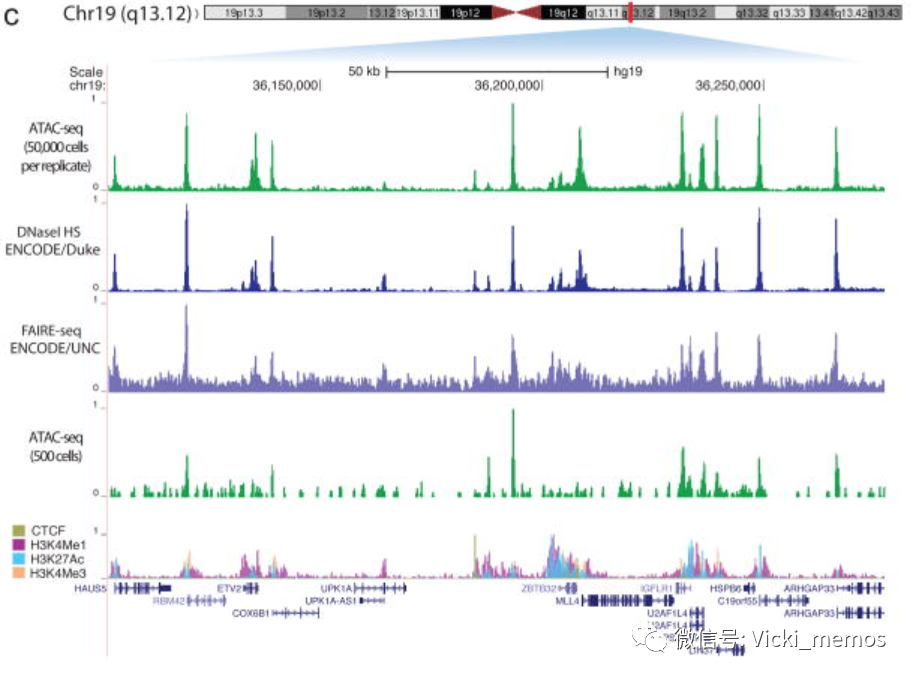
③Buenrostro, J., Giresi, P., Zaba, L. et al. Transposition of native chromatin for fast and sensitive epigenomic profiling of open chromatin, DNA-binding proteins and nucleosome position. Nat Methods 10, 1213–1218 (2013). https://doi.org/10.1038/nmeth.2688


往期回顾: